- DNA는 replication, transcription, translation 과정을 거쳐 단백질을 만든다. 첫 단계인 복제는 initiation, elongation, termination으로 이뤄진다.
- 보통 단백질은 Brca1처럼 쓴다.
암기
- (원핵) DNA pol 1은 RNA primer 제거 & DNA 메움
- (진핵) 선도가닥은 alpha-epsilon / 지연가닥은 alpha-delta
- primase는 DdRp 활성 / TERT는 RdDp 활성 푸딩과 타르트
* telomerase는 RNA와 TERT로 구성되며 3'-말단을 늘림
- ligase는 PD 결합
- Dam methylase는 메틸기를 붙여서 복제되도록 만듦 / SeqA는 막 복제된 애가 또 복제되지 않도록 해줌
자꾸 댐을 지으려고 했지만 세콰이어 나무가 막아섰음
- termiation은 Tus-Ter ~> top4 끝났다. 투투! 토사물!
DNA 기초
- 3' OH기와 5' phosphate기가 H2O 빠져나가며 phospho/diester bond로 연결된다.
- 이중가닥은 역평행으로 위치한다.
- AT 2중결합, GC 3중결합

DNA 복제
- 반보존적이고, replication of origin(진핵생물은 여러개, 대장균은 1개)에서 양방향으로 진행하고, DNA 합성은 5'~>3' 방향이다.
- replication of origin에서 양쪽으로 replication fork를 밀어나가며 이중나선을 분리한다.
- replication fork와 이동방향이 같으면 leading strand / 반대면 lagging strand (okazaki fragment를 형성)
DNA polymerase
1. template-directed DNA 합성 : 템플릿이 있어야 합성한다.
2. dNTP를 에너지원으로 : dNTP 잡아다가 pyrophosphate(인산기 2개) 떼어내며 발생하는 에너지로 합성한다.
3. 지속성(processivity) : DNA에서 떨어지기 전까지 여러 개의 nucleotide를 추가한다.
* 지속성을 주는 것이 도넛 모양의 sliding clamp(beta clamp)다. clamp loader가 도넛을 벌리고 DNA에 장착시키면 오랫동안 합성이 가능하다.
* 진핵생물에서는 beta clamp의 기능을 PCNA가 한다.
- 합성하다가 뭔가 잘못된 nucleotide를 끼워넣었다면 3-5 exo/nuclease가 작동하여 proof/reading(교정)을 수행한다. 결과적으로 10억~100억 nucleotide 중 1개의 error가 발생한다.
대장균은 DNA Pol1, 2, 3이 있다.
- 복제는 주로 3이 하고 / 1과 2는 repair에 관여한다.
- DNA pol 1은 5-3 exonuclease로 RNA primer를 제거하고, 동시에 DNA 삽입하는 nick translation이 일어난다.
동대문디지털플라자에 1등으로 도착한 닉 ~> DNA pol 1은 nick ~> RNA primer 제거와 DNA 삽입이 동시에 일어남 ~> proofreading은 3-5 exonuclease니까, RNA primer 제거는 5-3 exonuclease
- DNA pol 3은 여러 subunit을 갖는다. alpha가 polymerization, epsilon이 proofreading, theta가 안정화한다.
replisome
DNA 복제를 위한 종합선물세트다. 종류가 많다.
- DNA helicase (DnaB) : lagging strand의 template DNA(풀린 이중나선 중 아랫놈)에 결합해서 5-3 이동하며 이중나선의 수소결합을 자른다.
비상! 헬리콥터 조종수가 바지 지퍼를 풀어헤치며 달려온다 ~> DnaB, helicase, 지퍼 풀어헤침(이중나선 수소결합 분리) ~> 그리고 B의 다음인 DnaC는 helicase loader임

- SSB(single-strand binding) protein : helicase가 풀어헤친 단일가닥에 SSB가 결합하여 안정화시킨다. 지들끼리 꼬이는 re-annealing을 방지한다.
- topoisomerase : DNA를 벌리면 topological stress로 꼬임(supercoiling)이 발생한다.
* 1은 절단하고 ligation으로 다시 연결한다. 2는 ATP를 소모하여 supercoiling을 완화한다. 4는 그냥 분리한다.
- primase (DnaG) : DdRp에 해당한다. DNA pol이 작용하려면 3-OH기가 있어야 하니까 이를 위해 RNA primer를 합성해준다.
* 지연가닥은 이곳저곳에 primer를 심어야 하므로 선도가닥과 다르게 primase가 여러 번 작용한다.
지프 ~> DnaG, primase ~> 그러니까 RNA primer를 붙임

primer 제거, 오카자키 절편 연결
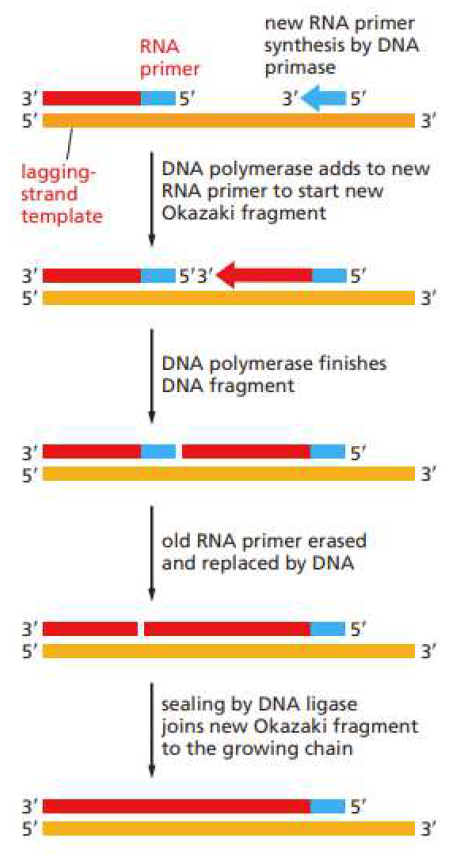
- DNA pol 1이 RNA primer를 제거하고, DNA ligase가 phosphodiester bond를 형성한다.
* 즉 원핵생물에서는 primase가 primer를 생성하고 / DNA polymerase 1이 primer를 제거한다.
실제 복제 과정
initiation
- oriC : R site와 / ATP 의존 I site로 나뉜다. R과 I site에 DnaA(복제 개시 단백질)가 결합하면 DUE가 불안정화된다.
A는 첫 알파벳이니까 oriC에 결합하는 첫 단계 (복제 개시 단백질)
I site는 I라서 소극적으로 개시함 (ATP라는 친구가 와줘야 함)
- helicase loader(DnaC)에 ATP가 결합 ~> DnaB hexamer가 분리 ~> replication fork로 가서 잘라먹음
- adenine은 Dam methylase에 의해 methylation되어 있어야 복제된다. ~> SeqA가 이를 막아놓는다.
elongation
- 선도가닥 : primase가 RNA primer 한번 붙이면 ~> DNA pol 3이 nucleotide 첨가
- 지연가닥 : primase가 RNA primer 계속 붙이면 ~> RNA primer를 포함하는 DNA 조각인 오카자키 절편이 DNA pol 3에 의해 만들어지고 ~> DNA pol 1이 nick translation 진행하고 ~> DNA ligase가 절편 연결함
* fragment마다 sliding clamp 가짐
termination
- 원형 DNA의 경우, oriC 반대편에 Ter sequence가 여럿 있음
- Tus 단백질과 결합 ~> Tus-Ter 복합체 형성해서 한쪽 방향으로의 합성만 통과시킴 ~> 두 fork 중 한쪽 방향이 폭주하는 것을 막아줌
즉 nonpermissive site에서는 Tus-Ter sequence가 복제를 멈춤
- 복제 종료 후 원형고리 2개가 얽힌 모습의 catenane 구조 ~> DNA topoisomerase 4가 분리
eukaryotic replication
- oriC가 많고 각각의 복제 구역을 replication bubble이라 함
- prokaryote의 SSB에 해당하는 RPA(replication protein A)를 가짐
* SSB처럼 nuclease 막고 reannealing 막는 것에 더해 DNA repair도 관여함
DNA pol
alpha : DNA 합성(proofreading 기능 없음)
beta : pol2(repair)
gamma : mtDNA 복제
delta : pol3(지연)
* 지연가닥에서 pol delta가 PCNA와 결합 ~> okazaki fragment 형성
epsilon : pol3(선도)
세계를 선도하는 엡실론
- 지연가닥에서는 RNase H, FEN1이 작용하여 RNA primer를 떨어트리고 ~> DNA ligase가 nick을 연결하여 복제 완성한다.
- PCNA는 선도가닥(pol epsilon) 또는 지연가닥(pol delta)과 pol을 꽉 결합해준다.
telomere
- 지연가닥의 RNA primer 제거로 5-말단이 짧아진다.
- telomerase는 RNA와 TERT(단백질이며 RdDp)로 구성된다.
푸딩과 타르트 ~> primase는 D로 시작(DdRp)이고 TERT는 R로 시작(RdDp)
- 5말단이 짧아지는데 TERT는 3말단을 연장한다. ~> telomerase는 DNA 짧아지는 속도를 늦출 뿐 멈추지는 못한다.
- hTERT 활성 ~> TERT와 telomerase 촉진 ~> 암세포
항암제 (읽어만 보기)
- 독쏘루비신(doxorubicin)은 topo 2 억제하여 이중나선 안정성 방해
- 에또포사이드(etoposide)도 topo 2 억제
- 씨프로플록싸씬(ciprofloxacin)은 gyrase(원핵 topo 2)와 topo 4 억제하여 DNA 절단 유도
DNA 복제 : 원핵생물 및 진핵생물의 기전과 조절
원핵생물(대장균, E. coli)과 진핵생물(사람)의 DNA 복제 과정을 중심으로, 핵심 효소의 기능, 복제 단계별 기전, 그리고 복제 조절 및 말단 복제 문제 등을 종합적으로 분석한다.
--------------------------------------------------------------------------------
1. 핵심 요약 (Executive Summary)
DNA 복제는 생명체의 유전 정보를 보존하고 전달하는 필수적인 과정으로, 반보존적(semi-conservative) 방식과 양방향성(bidirectional)을 띤다. 본 분석의 주요 결론은 다음과 같다.
- 복제 원칙: DNA 합성은 항상 5' ~> 3' 방향으로 진행되며, 선도 가닥(leading strand)은 연속적으로, 지체 가닥(lagging strand)은 오카자키 절편(Okazaki fragment)을 통해 불연속적으로 합성된다.
- 원핵생물 복제: 단일 복제 원점(oriC)에서 시작하며, DnaA 단백질과 메틸화(methylation) 상태에 의해 복제 개시가 정교하게 조절된다. Tus-Ter 복합체를 통해 특정 지점에서 복제가 종료되며, Topoisomerase IV가 얽힌 염색체를 분리한다.
- 진핵생물 복제: 선상(linear) 염색체 구조로 인해 여러 복제 원점이 존재하며, 중합효소 alpha, delta, epsilon이 복제 역할을 분담한다. 특히 말단부인 텔로미어(telomere)의 단축 문제를 해결하기 위해 텔로머레이스(telomerase)가 작용한다.
- 교정 및 안정성: DNA 중합효소의 3' ~> 5' exonuclease 활성을 통한 교정(proofreading) 기능과 sliding clamp를 이용한 지속성(processivity) 확보가 복제 정확도의 핵심이다.
--------------------------------------------------------------------------------
2. DNA 구조 및 명명 규칙
2.1 뉴클레오타이드(Nucleotide) 구조 및 결합
- 당 번호 지정: 리보스(ribose) 탄소는 1'부터 5'까지 번호를 매긴다. 1'은 염기(base)와 결합하고, 2'은 RNA(OH)와 DNA(H)를 구분하며, 3'은 인접 뉴클레오타이드와 결합한다. 5'에는 인산기(PO_4^-)가 결합한다.
- DNA 백본(Backbone): 인접한 뉴클레오타이드의 3'-OH기와 5'-인산기 사이의 **포스포디에스테르 결합(Phosphodiester bond)**을 통해 형성된다.
- 역평행 구조: 두 가닥의 DNA는 서로 반대 방향(antiparallel)으로 위치하며, 염기 간 수소결합(A-T는 2개, G-C는 3개)을 통해 연결된다.
2.2 유전자 및 단백질 명명법
| 구분 | 박테리아(원핵) | 사람(진핵) |
| 유전자(Gene) | 소문자 3개 이탤릭체 (예: dnaA, uvr) | 모두 대문자 이탤릭체 (예: BRCA1, HK1) |
| 단백질(Protein) | 첫 글자 대문자, 정자 (예: DnaA) | 유전자 기반 표기 또는 약자기반 대문자 (예: Brca1, PCNA) |
--------------------------------------------------------------------------------
3. 원핵생물의 DNA 복제 기전 (E. coli 모델)
3.1 복제 개시(Initiation) 및 조절
- 복제 원점(oriC): 대장균은 단일 복제 원점을 가지며, 고친화도 DnaA 결합 부위인 R site와 ATP 결합형 DnaA가 선택적으로 작용하는 I site로 구성된다.
- 개시 단백질(DnaA): ATP와 결합하여 활성화된 DnaA oligomer는 DNA를 휘게 만들어 DUE(DNA Unwinding Element) 부위를 풀어줌으로써 헬리케이스 등의 접근을 돕는다.
- 복제 조절(Methylation): 복제 직후 DNA는 반메틸화(hemimethylation) 상태가 된다. 이때 SeqA 단백질이 oriC에 결합하여 Dam 메틸화 효소의 접근을 차단함으로써, 한 복제 주기 내에 복제가 중복 개시되는 것을 방지한다.
3.2 복제 신장(Elongation)의 주요 효소
- DNA Helicase (DnaB): 이중나선을 풀며 지체 가닥의 주형을 따라 5' \rightarrow 3' 방향으로 이동한다.
- DNA Polymerase III: 주 복제 효소로, \beta clamp(sliding clamp)에 의해 주형 DNA에 고정되어 높은 지속성을 가진다. \beta clamp는 clamp loader complex에 의해 ATP 의존적으로 장착된다.
- Primase: DNA 합성에 필요한 3'-OH기를 제공하기 위해 짧은 RNA 프라이머를 합성한다.
- DNA Polymerase I: 5' \rightarrow 3' exonuclease 활성으로 RNA 프라이머를 제거하고 DNA를 채우는 **닉 번역(Nick translation)**을 수행한다.
- DNA Ligase: 절편 사이의 포스포디에스테르 결합을 형성하여 최종적으로 연결한다.
3.3 복제 종료(Termination)
- Tus-Ter 복합체: 특정 방향으로만 복제 분기점(replication fork)의 이동을 허용하는 polar site이다. 허용되지 않는 방향에서 접근하는 복제 복합체를 물리적으로 차단하여 복제를 종료시킨다.
- Catenane 구조 분리: 복제 완료 후 서로 얽힌 딸염색체는 Topoisomerase IV에 의해 두 가닥 절단 및 재연결 과정을 거쳐 분리된다.
--------------------------------------------------------------------------------
4. 진핵생물의 DNA 복제와 텔로미어
4.1 진핵생물 복제의 특징
진핵생물은 원핵생물에 비해 방대한 염기서열을 복제하기 위해 하나의 염색체에 여러 개의 **복제 기포(Replication bubble)**를 형성한다.
- 주요 중합효소:
- Pol \epsilon: 선도 가닥 합성 주도.
- Pol \delta: 지체 가닥 합성 주도. 오카자키 절편 합성 시 앞선 프라이머를 플랩(flap) 형태로 밀어낸다.
- Primase-Pol \alpha 복합체: RNA 프라이머와 초기 짧은 DNA 서열을 합성한다.
- Pol \gamma: 미토콘드리아 DNA 복제 담당.
- 오카자키 절편 처리: RNase H가 RNA 프라이머를 제거하고, 남은 마지막 리보뉴클레오타이드는 **FEN 1(flap endonuclease 1)**이 제거한다.
4.2 텔로미어(Telomere)와 말단 복제 문제
- 문제점: 지체 가닥의 마지막 RNA 프라이머가 제거된 후, 5'-말단이 짧아지는 문제가 발생한다. 이는 복제가 반복될수록 염색체가 점차 짧아지게 하여 세포 노화나 사멸(apoptosis)을 유도한다.
- 텔로머레이스(Telomerase): RNA 의존성 DNA 중합효소(hTERT) 활성을 가져, 자신의 RNA를 주형으로 사용하여 부모 DNA의 3'-말단을 연장한다.
- 암세포와의 연관성: 암세포는 hTERT 유전자를 재활성화하여 텔로미어를 유지함으로써 무한 증식(immortalization)이 가능해진다. 이는 암세포의 주요 특징 중 하나이다.
--------------------------------------------------------------------------------
5. DNA 복제 관련 주요 단백질 및 효소 비교 요약
| 기능 | 원핵생물 (E. coli) | 진핵생물 (사람) |
| 주 중합효소 (선도 가닥) | DNA Polymerase III | DNA Polymerase \epsilon |
| 주 중합효소 (지체 가닥) | DNA Polymerase III | DNA Polymerase \delta |
| Sliding Clamp | \beta clamp | PCNA |
| 프라이머 제거 | DNA Polymerase I | RNase H, FEN 1 |
| 초기 개시 조절 | SeqA (메틸화 차단) | 복제 원점 다수 존재 |
| 초과 꼬임(Supercoil) 완화 | DNA Gyrase 등 | Topoisomerase I, II |
| 말단 문제 해결 | 원형 DNA (해당 없음) | Telomerase |
--------------------------------------------------------------------------------
6. 결론 및 임상적 의의
DNA 복제 과정의 이해는 생물학적 기초 지식을 넘어 임상적으로도 중요하다. Topoisomerase 억제제(Adriamycin, Etoposide, Ciprofloxacin 등)는 항암제나 항생제로 활용되며, 텔로머레이스 활성 조절은 노화 및 암 치료 연구의 핵심 표적이다. 복제의 정확성을 유지하는 중합효소의 교정 기능과 각 단백질의 정교한 상호작용은 생명의 연속성을 보장하는 핵심 기전으로 평가된다.
'기초의학 > 생화학' 카테고리의 다른 글
| [생화학] RNA metabolism (0) | 2026.02.10 |
|---|---|
| [생화학] DNA repair (0) | 2026.02.10 |
| [생화학] Integration of metabolism (0) | 2026.01.31 |
| [생화학] Nucleotide metabolism (0) | 2026.01.31 |
| [생화학] 아미노산 대사 (0) | 2026.01.31 |